Molekul DNA dalam suatu sel dapat diekstraksi atau diisolasi untuk berbagai macam keperluan seperti amplifikasi dan analisis DNA melalui elektroforesis. Isolasi DNA dilakukan dengan tujuan untuk memisahkan DNA dari bahan lain seperti protein, lemak, dan karbohidrat. Prisnsip utama dalam isolasi DNA ada tiga yakni penghancuran (lisis), ektraksi atau pemisahan DNA dari bahan padat seperti selulosa dan protein, serta pemurnian DNA (Corkill dan Rapley, 2008; Dolphin, 2008). Menurut Surzycki (2000), ada beberapa hal yang perlu diperhatikan dalam proses isolasi DNA antara lain harus menghasilkan DNA tanpa adanya kontaminan seperti protein dan RNA; metodenya harus efektif dan bisa dilakukan untuk semua spesies metode yang dilakukan tidak boleh mengubah struktur dan fungsi molekul DNA; dan metodenya harus sederhana dan cepat.
Isolasi DNA tanaman, isolasi DNA buah, isolasi DNA bakteri, dan isolasi DNA hewan pada dasarnya memiliki prinsip yang sama. Prisnsip isolasi DNA pada berbagai jenis sel atau jaringan pada berbagai organisme pada dasarnya sama namun memiliki modifikasi dalam hal teknik dan bahan yang digunakan. Bahkan beberapa teknik menjadi lebih mudah dengan menggunakan kit yang diproduksi oleh suatu perusahaan sebagai contoh kit yang digunakan untuk isolasi DNA pada tumbuhan seperti Kit Nucleon Phytopure sedangkan untuk isolasi DNA pada hewan digunakan GeneJETTM Genomic DNA Purification Kit. Namun tahapan-tahapan isolasi DNA dalam setiap langkahnya memiliki protokol sendiri yang disesuaikan dengan keperluan. Penggunaan teknik isolasi DNA dengan kit dan manual memiliki kelebihan dan kekurangan. Metode konvensional memiliki kelebihan harga lebih murah dan digunakan secara luas sementara kekurangannya membutuhkan waktu yang relatif lama dan hasil yang diperoleh tergantung jenis sampel.
Silahkan baca juga: Isolasi RNA
1. Tahapan Lisis
Tahap pertama dalam isolasi DNA adalah proses perusakan atau penghancuran membran dan dinding sel. Pemecahan sel (lisis) merupakan tahapan dari awal isolasi DNA yang bertujuan untuk mengeluarkan isi sel (Holme dan Hazel, 1998). Tahap penghancuran sel atau jaringan memiliki beberapa cara yakni dengan cara fisik seperti menggerus sampel dengan menggunakan mortar dan pestle dalam nitrogen cair atau dengan menggunakan metode freezing-thawing dan iradiasi (Giacomazzi et al., 2005). Cara lain yakni dengan menggunakan kimiawi maupun enzimatik. Penghancuran dengan menggunakan kimiawi seperti penggunaan detergen yang dapat melarutkan lipid pada membran sel sehingga terjadi destabilisasi membran sel (Surzycki, 2000). Sementara cara enzimatik seperti menggunakan proteinase K seperti untuk melisiskan membran pada sel darah (Khosravinia et al., 2007) serta mendegradasi protein globular maupun rantai polipeptida dalam komponen sel (Brown, 2010; Surzycki (2000).
Pada proses lisis dengan menggunakan detergen, sering digunakan sodium dodecyl sulphate (SDS) sebagai tahap pelisisan membran sel. Detergen tersebut selain berperan dalam melisiskan membran sel juga dapat berperan dalam mengurangi aktivitas enzim nuklease yang merupakan enzim pendegradasi DNA (Switzer, 1999). Selain digunakan SDS, detergen yang lain seperti cetyl trimethylammonium bromide (CTAB) juga sering dipakai untuk melisiskan membran sel pada isolasi DNA tumbuhan (Bettelheim dan Landesberg, 2007). Parameter keberhasilan dalam penggunaan CTAB bergantung pada beberapa hal. Pertama, Konsentrasi NaCl harus di atas 1.0 M untuk mencegah terbentuknya kompleks CTAB-DNA. Karena jumlah air dalam pelet sel sulit diprediksi, maka penggunaan CTAB sebagai pemecah larutan harus dengan NaCl dengan konsentrasi minimal 1.4 M. Kedua, ekstrak dan larutan sel yang mengandung CTAB harus disimpan pada suhu ruang karena kompleks CTAB-DNA bersifatinsolublepada suhu di bawah 15°C. Ketiga, penggunaan CTAB dengan kemurnian yang baik akan menentukan kemurnian DNA yang didapatkan dan dengan sedikit sekali kontaminasi polisakarida. Setelah ditambahkan CTAB, sampel diinkubasikan pada suhu kamar. Tujuan inkubasi ini adalah untuk mencegah pengendapan CTAB karena CTAB akan mengendap pada suhu 15°C. Karena efektivitasnya dalam menghilangkan polisakarida, CTAB banyak digunakan untuk purifikasi DNA pada sel yang mengandung banyak polisakarida seperti terdapat pada sel tanaman dan bakteri gram negatif seperti Pseudomonas, Agrobacterium, dan Rhizobium (Surzycki, 2000).
Dalam penggunaan buffer CTAB seringkali ditambahkan reagen-reagen lain seperti NaCl, EDTA, Tris-HCl, dan 2-mercaptoethanol. NaCl berfungsi untuk menghilangkan polisakarida sementara 2-mercaptoethanol befungsi untuk menghilangkan kandungan senyawa polifenol dalam sel tumbuhan (Ranjan et al., 2010). 2-mercaptoethanol dapat menghilangkan polifenol dalam sel tanaman dengan cara membentuk ikatan hidrogen dengan senyawa polifenol yang kemudian akan terpisah dengan DNA (Lodhi et al., 1994). Senyawa polifenol perlu dihilangkan agar diperoleh kualitas DNA yang baik (Moyo et al., 2008). Polifenol juga dapat menghambat reaksi dari enzim Taq polimerase pada saat dilakukan amplifikasi. Disamping itu polifenol akan mengurangi hasil ektraksi DNA serta mengurangi tingkat kemurnian DNA (Porebskiet al., 1997). Penggunaan 2-mercaptoethanol dengan pemanasan juga dapat mendenaturasi protein yang mengkontaminasi DNA (Walker dan Rapley, 2008).
Konsentrasi dan pH dari bufer yang digunakan harus berada dalam rentang pH 5 sampai 12. Larutan buffer dengan pH rendah akan mengkibatkan depurifikasi dan mengakibatkan DNA terdistribusi ke fase fenol selama proses deproteinisasi. Sedangkan pH larutan yang tinggi di atas 12 akan mengakibatkan pemisahan untai ganda DNA. Fungsi larutan buffer adalah untuk menjaga struktur DNA selama proses penghancuran dan purifikasi sehingga memudahkan dalam menghilangkan protein dan RNA serta mencegah aktivitas enzim pendegradasi DNA dan mencegah perubahan pada molekul DNA. Untuk mengoptimalkan fungsi larutan buffer, dibutuhkan konsentrasi, pH, kekuatan ion, dan penambahan inhibitor DNAase dan detergen (Surzycki 2000).
2. Tahapan Ekstraksi
Pada tahapan ekstraksi DNA, seringkali digunakan chelating agent seperti ethylenediamine tetraacetic acid (EDTA) yang berperan menginaktivasi enzim DNase yang dapat mendenaturasi DNA yang diisolasi, EDTA menginaktivasi enzim nuklease dengan cara mengikat ion magnesium dan kalsium yang dibutuhkan sebagai kofaktor enzim DNAse (Corkill dan Rapley, 2008). DNA yang telah diekstraksi dari dalam sel selanjutnya perlu dipisahkan dari kontaminan komponen penyusun sel lainnya seperti polisakarida dan protein agar DNA yang didapatkan memiliki kemurnian yang tinggi. Fenol seringkali digunakan sebagai pendenaturasi protein, ekstraksi dengan menggunakan fenol menyebabkan protein kehilangan kelarutannya dan mengalami presipitasi yang selanjutnya dapat dipisahkan dari DNA melalui sentrifugasi (Karp, 2008). Bettelheim dan Landesberg (2007) menyebutkan bahwa setelah sentrifugasi akan terbentuk 2 fase yang terpisah yakni fase organik pada lapisan bawah dan fase aquoeus (air) pada lapisan atas sedangkan DNA dan RNA akan berada pada fase aquoeus setelah sentrifugasi sedangkan protein yang terdenaturasi akan berada pada interfase dan lipid akan berada pada fase organik (Gambar 1). Selain fenol, dapat pula digunakan campuran fenol dan kloroform atau campuran fenol, kloroform, dan isoamil alkohol untuk mendenaturasi protein. Ekstrak DNA yang didapat seringkali juga terkontaminasi oleh RNA sehingga RNA dapat dipisahkan dari DNA ekstrak dengan cara pemberian RNAse (Birren, et al., 1997; Clark, 2010).
Gambar 1. Asam nukleat berada pada lapisan air setelah disentrifugasi pada tahapan ekstraksi (Clark, 2010).
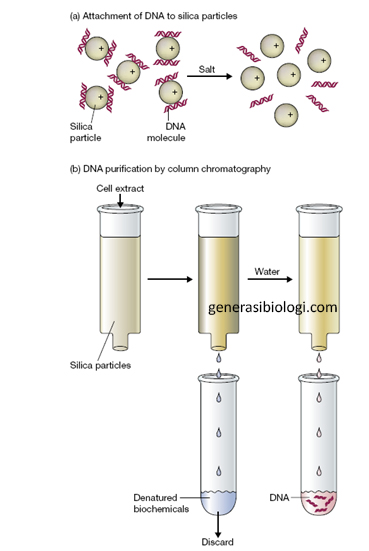
3. Tahapan Pemisahan DNA
Gambar 2. Proses pufrifikasi DNA dengan menggunakan metode silika dan kolom kromatografi (a) proses pengikatan DNA ke silika dengan bantuan perubahan konsentrasi garam, (b) DNA dielusi untuk memperoleh DNA (Brown, 2010).
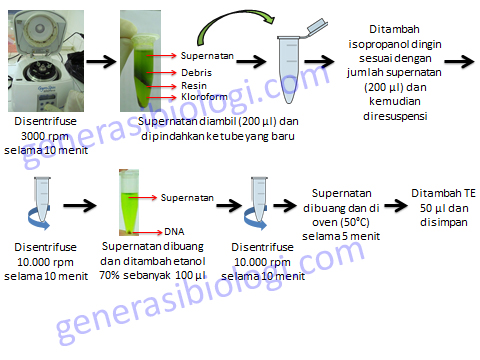
Kit Isolasi DNA
Isolasi DNA juga dapat dilakukan dengan menggunakan kit yang sudah diproduksi oleh beberapa perusahan untuk mempermudah dan mempercepat proses isolasi DNA. Kit isolasi juga disesuaikan dengan kebutuhan oleh konsumen dan jenis sel yang akan digunakan. Berikut adalah bagan contoh isolasi DNA tanaman dengan menggunakan Kit Nucleon Phytopure yang disajikan pada Gambar 3.
Referensi:
- Ausubel, F. M. et al. 2003. Current Protocols in Molecular Biology.
- Bettelheim & Landesberg. 2007. Laboratory experiments for general organic and biochemistry.
- Clark, Melody S. 1997. Plant Molecular Biology : A laboratory manual.
- Dolphin, W. D. 2008. Biological Investigations.
- Hoelzel, A. R. 1992. Molecular Genetic Analysis of Populations.
- Holme, D. J. & Hazel P. 1998. Analytical Biochemistry.
- Karp, Gerald. 2008. Cell and Molecular Biology.
- Keller, G. H. & Mark M. M. 1989. DNA probes.
- Khosravinia, H. & Ramesha, K. P. 2007. Influence of EDTA and magnesium on DNA extraction from blood samples and specificity of polymerase chain reaction. African Journal of Biotechnology 6 (3), pp. 184-187
- Surzycki, S. 2000. Basic techniques in molecular biology.
- Switzer. 1999. Experimental biochemistry.
- Verkuil, E. v. P., Alex van B., & John P. H. 2008. Principles and technical aspects of PCR amplification.
- Walker, J. M. & Ralph R. 2008. Molecular Biomethods Handbook.












Leave a Reply